Neuroanatomie der Drosophilalarve
Motivation
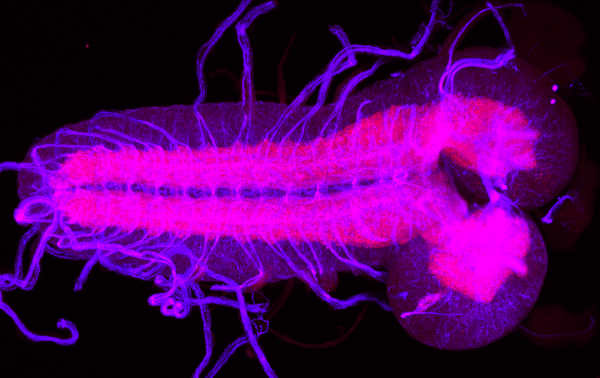
Das zentrale Nervensystem der Drosophilalarve ist mit nur ca. 10.000 Neuronen klein genug, um eine anatomische Rekonstruktion aller Neuronen und ihrer Konnektivität zu ermöglichen. Gleichzeitig sind die Larve und ihr Verhalten auch schon komplex genug, um für die Neuroethologie von Interesse zu sein, und Drosophila ist der wohl bedeutendste Modellorganismus in der Biologie.
Wissenschaftliche Fragestellungen
Für die neurobiologische Forschung am larvalen Drosophilagehirn entwicklen wir Methoden zur Auswertung von licht- und elektronenmikroskopischen Daten, sowie von aus letzteren rekonstruierten 3D-Neuronenstrukturen („neuron skeletons“).
Insbesondere haben wir aus lichtmikroskopischen Aufnahmen ein Standardgehirn (zentrales Nervensystem) der Drosophilalarve erstellt, und unsere Software larvalign ermöglicht die Registrierung neuer Scans in das Koordinatensystem des Standardgehirns (Muenzing et al., 2018). Desweiteren arbeiten wir an einer multimodalen Registrierung zwischen licht- und elektronenmikroskopischen Gehirnaufnahmen.
Auf der Ebene der rekonstruierten Einzelneuronen haben wir Analyse- und Visualisierungswerkzeuge für die neuroanatomische Datenauswertung entwickelt: Topologisch korrekte, aber vereinfachte, Repräsentationen der 3D-Neuronstruktur in Form von 2D-Dendrogrammen erlauben eine übersichtliche Darstellung morphologisch komplexer Neuronen und deren Konnektivität in lokalen Netzwerken (Strauch et al, 2018, Schleyer et al., 2020).
Kooperationspartner
- Prof. Dr. Andreas Stephan Thum, Institut für Biologie, Universität Leipzig
- Dr. Katja Bühler, VRVis Zentrum für Virtual Reality und Visualisierung Forschungs-GmbH, Wien
- Prof. Dr. Volker Hartenstein, Department of Molecular, Cell and Developmental Biology, University of California, Los Angeles
Drittmittel
- DFG Sachbeihilfe, „Das larvale 4D Standardgehirn von Drosophila melanogaster analysiert auf Einzelzell-Ebene“, Projektnr. 266382180
- DFG Sachbeihilfe, „Larvalbrain2.0: Eine Forschungsplattform für das larvale Gehirn von Drosophila melanogaster“, Projektnr. 441181781
Kontakt
Veröffentlichungen

Identification of dopaminergic neurons that can both establish associative memory and acutely terminate its behavioral expression
In: Journal of Neuroscience 40 (31)





